サンプル中の細菌について、単離・培養せず、DNAから分析します
概要
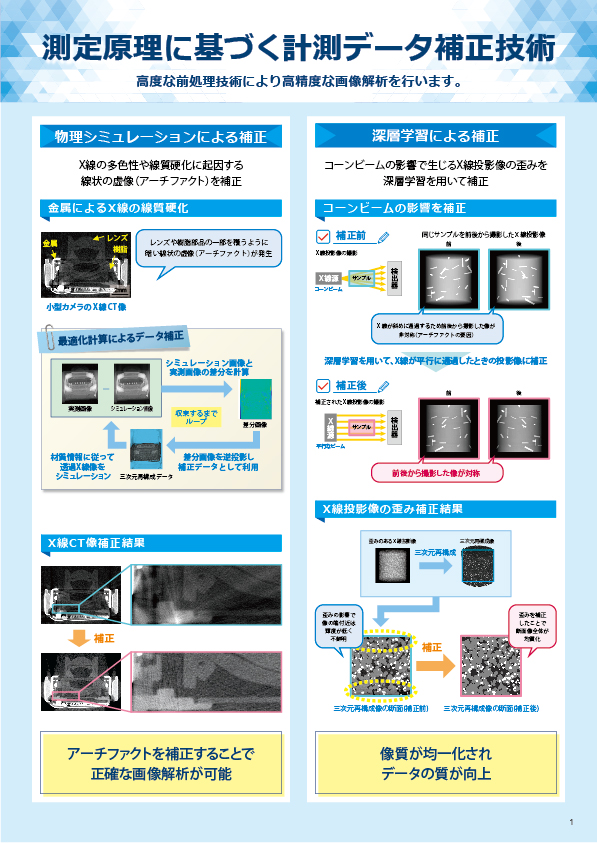
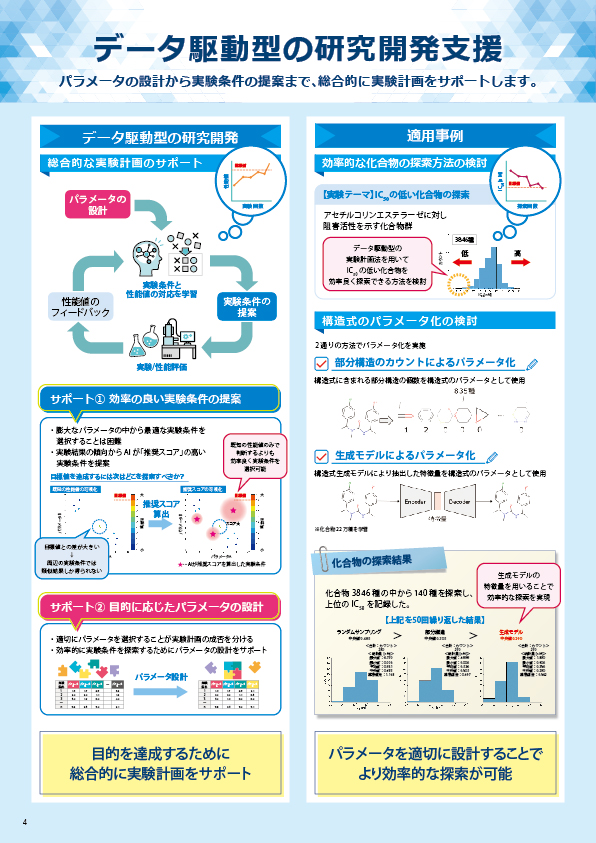
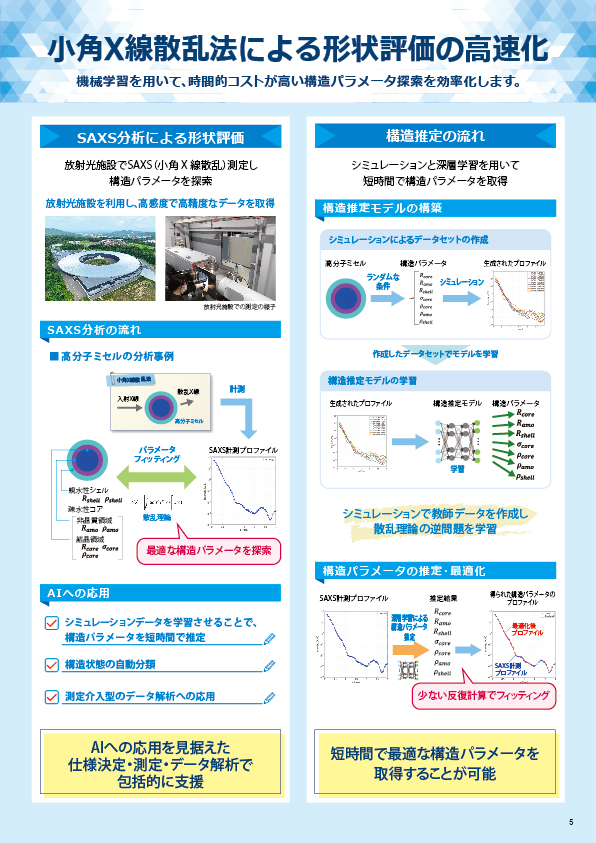
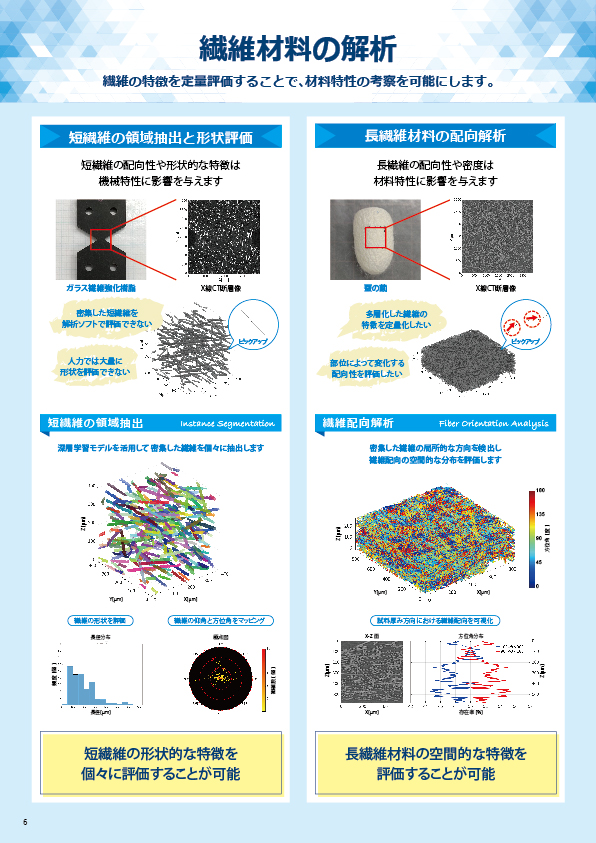
食品の細菌検査等で実施される菌数の測定は、培養してコロニー数をカウントすることで算出しますが、この方法では培養に時間を要し、また、難培養性の菌では評価ができません。一方、リアルタイムPCR法では、培養せずにサンプルから直接DNAを抽出することで、目的の菌の存在量(DNAコピー数)を調べることができます。本資料では、培養が容易な大腸菌を用いて、培養してカウントした菌数と、リアルタイムPCR法で測定したコピー数を比較した事例を紹介します。
測定例
大腸菌培養液を段階希釈してコロニー数カウントを行い、菌数を算出しました。それと同時に、大腸菌培養液それぞれからDNA抽出を行い、リアルタイムPCR法にてふたつのターゲット遺伝子(※)の測定を行い、結果を比較しました。
※測定したターゲット遺伝子
・uidA: シングルコピー遺伝子→ひとつの細胞にひとつの領域
・16S rRNA: 複数コピー遺伝子→ひとつの細胞にふたつ以上の領域
大腸菌では7コピーとされている
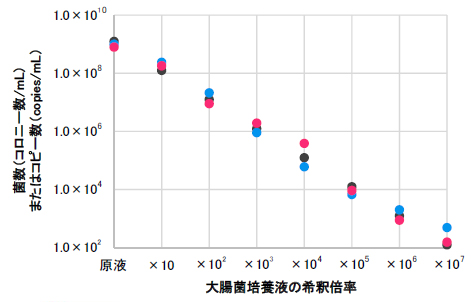 |
● 16S rRNA コピー数(copies/mL)を7で割ったもの ● uidA コピー数(copies/mL) ● 菌数(コロニー/mL) |
| 左のグラフにおいて、菌数(●)と比べ、16S rRNA コピー数/7(●)とuidA コピー数(●)のどちらも1オーダー以上のずれは見られませんでした。 これらの結果より、コピー数から菌数を推測できると考えられます。 |